2020年12月8日,我院黄俊实验室在Molecular Cell杂志上在线发表了题为“The ZATT-TOP2A-PICH axis drives extensive replication fork reversal to promote genome stability”的研究文章。该研究揭示了复制叉翻转(Fork reversal)过程中通过ZATT-TOP2A-PICH轴调控复制叉进一步翻转的分子机制,提出了复制叉翻转的两步调控模型。
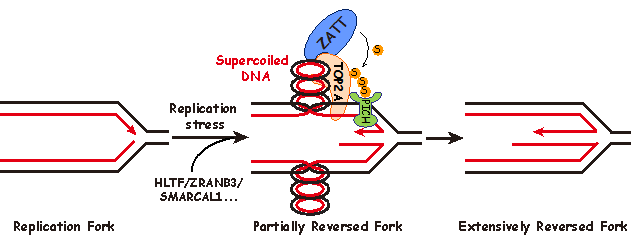
DNA的精确复制对于维持基因组稳定性至关重要。然而复制叉时常会遭受来自细胞内外的复制压力而停滞,如果无法及时重新起始,将造成复制叉崩塌,影响基因组稳定性甚至导致细胞死亡。1976年Higgins N. Patrick等人在研究复制相关的损伤修复时,在哺乳动物细胞中观察到了一种Holliday Junction的结构。他们猜测该结构形成的原因是复制叉停滞后,两条新合成的DNA子链与亲代DNA链解开后发生退火而翻转,进而将正常的复制叉结构重塑成Holliday Junction结构(图一),该过程也被称为复制叉翻转。由于Holliday Junction结构的形状与鸡爪相似,生物化学教科书中也通常将其称为“鸡爪结构 (chicken foot)”。受检测技术的限制,直到2002年José M. Sogo等人才在检验点缺陷的酵母细胞中观察到“鸡爪结构”,“鸡爪结构”也因此被认为是复制失败的副产物,其生理意义一直存在争议。近年来研究表明,在高等真核生物细胞中,复制叉翻转是由PARP1介导的应对复制压力的关键调控机制,酵母中由于缺乏PARP基因,因而在正常生理条件下极少能够观察到“鸡爪结构”的存在。
图一:新合成的链与亲代DNA链解开产生拓扑张力
该研究首次提出了“鸡爪结构”是通过两步级联反应而形成的新模型(图一)。第一步,在复制叉遭遇复制压力时,复制叉发生停滞,由转位酶HLTF、ZRANB3、SMARCAL1等蛋白催化复制叉的初始翻转,同时在复制叉后方新合成的DNA双链上产生拓扑张力;第二步,拓扑异构酶TOP2A释放拓扑张力,并通过SUMO化修饰招募转位酶PICH促进复制叉的深度翻转。进一步的功能研究表明,复制叉的深度翻转对于维持基因组稳定性至关重要。
黄俊博士实验室的博士研究生田甜、卜敏、陈旭、丁林丽和阳玉兰为论文共同第一作者,黄俊教授为通讯作者。该研究工作也得到了北京大学李晴教授的大力支持。该研究受到国家科技部重点研发计划、国家自然科学基金、霍英东青年教师基金等项目的资助。
原文链接:https://doi.org/10.1016/j.molcel.2020.11.007